AGENT BRAND
品牌專題富集組蛋白或轉(zhuǎn)錄因子(TF)的復合DNA在體內(nèi),然后下一代測序提供了一個有利的工具,研究全基因組蛋白質(zhì)-DNA相互作用。它允許分析與活細胞中DNA序列結(jié)合的特定蛋白質(zhì)。這樣的分析要求該方法可靠地鑒定真正的靶蛋白富集區(qū)域,特別是來自有限的細胞樣品。這些樣品可以包括從組織中分離的稀有細胞群、從整個細胞群分選的特定細胞和原代培養(yǎng)的亞群細胞如胚胎細胞。此外,該方法應確保富集的DNA含有最少的背景,并且蛋白質(zhì)-DNA結(jié)合區(qū)的作圖具有最小偏差和高分辨率。已經(jīng)使用了很長一段時間來實現(xiàn)該目標的主要方法是染色質(zhì)免疫沉淀,然后是測序(ChIP-Seq)。然而,ChIP的主要局限性在于,它需要1)大量的輸入材料,細胞或組織,以產(chǎn)生超過背景噪聲的足夠強的信號;和2)在初始固定步驟期間交聯(lián)。有幾種先進的方法可用于ChIP-Seq,具有減少的細胞數(shù)量或增加的分辨率。這些方法包括ChIP-exo和ChIPmentation。ChIP-exo提供了高分辨率的映射,但耗時并且需要充足的輸入細胞供應。雖然ChIP片段化使用轉(zhuǎn)座酶和測序相容的銜接子以使得能夠在ChIP過程中整合連接,但其遵循傳統(tǒng)上緩慢(2天)的ChIP程序并且不能實現(xiàn)高分辨率作圖。CUT RUN(Cleavage Under Target Release Using Nuclease)是為了將捕獲的靶蛋白/DNA復合物從有限的生物材料中釋放出來,用于蛋白質(zhì)-DNA相互作用的作圖,它顯著提高了作圖分辨率。然而,CUT RUN需要昂貴的PA/Mnase融合蛋白,其具有顯著的A/T序列偏差,導致靶蛋白相互作用的DNA區(qū)域譜嚴重受MNase消化水平的影響。
據(jù)今年3月份發(fā)布在ResearchSquare的一項研究,佛羅里達的科學家使用CUT&RUN技術(shù),建立了眼球晶狀體中HIF1α結(jié)合位點的全基因組圖,文章鏈接:https://assets.researchsquare.com/files/rs-247248/v1/83c34fd6-e42a-491b-8828-247ace7a4fb8.pdf?c=1631877386

我們知道,基因表達可以通過許多不同的機制進行調(diào)節(jié),包括轉(zhuǎn)錄因子、組蛋白和其他DNA結(jié)合蛋白。繪制出DNA和蛋白質(zhì)之間的相互作用圖譜,對于理解基因激活或抑制以及其他細胞過程至關(guān)重要。
傳統(tǒng)上,可以通過進行染色質(zhì)免疫沉淀和測序(ChIP-seq)來分析這些相互作用。但是這種方法需要大量的起始材料才能產(chǎn)生足夠強的信號以消除背景噪聲,并且經(jīng)常返回假陽性信號。同時,ChIP-seq還需要優(yōu)化的超聲處理來破碎染色質(zhì),這可能非常耗時并可能導致樣品損失。
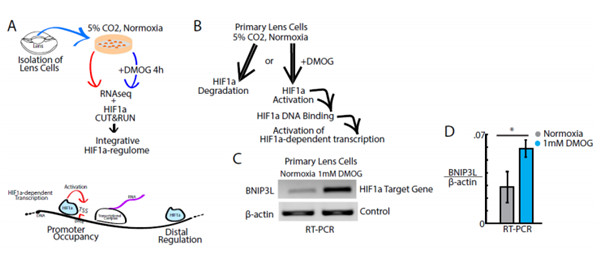
在最近的一項研究中,佛羅里達大西洋大學和國家糖尿病、消化和腎臟疾病研究所的科學家們利用CUT&RUN技術(shù)建立了一個功能性全基因組圖譜,該圖譜是一種稱為缺氧誘導因子的蛋白質(zhì)復合物的特異性結(jié)合位點—HIF1α,位于人眼的晶狀體中。該團隊表示選擇CUT&RUN而不是ChIP-seq分析,是因為前者不需要DNA-蛋白質(zhì)交聯(lián)。此外,與ChIP-seq相比,前者成功實驗所需的細胞計數(shù)極低。
正常而言,隨著出生后眼睛的發(fā)育,提供健康血液供應的血管隨著時間的推移開始萎縮。結(jié)果,眼睛中的氧氣含量穩(wěn)步下降,造成缺氧環(huán)境。HIF1α作為一種蛋白質(zhì)復合物,可調(diào)節(jié)身體對缺氧環(huán)境的反應,這意味著它可以在晶狀體細胞發(fā)育和體內(nèi)平衡中發(fā)揮作用。
研究人員首先選擇培養(yǎng)10天左右的大的WhiteLeghorn雞胚胎中分離出晶狀體細胞。收獲的細胞用稱為DMOG的HIF1α激活劑處理4小時,并用ConA包被的磁珠固定細胞核。之后,樣品被分為兩組:一組用HIF1α抗體處理,另一組用IgG抗體處理。將pA/MNase添加到樣品中以啟動碎裂。這種融合蛋白在與感興趣的蛋白質(zhì)相互作用的特定區(qū)域剪切DNA——在這種情況下,該蛋白質(zhì)是HIF1α。通過向樣品中加入CaCL2溶液來激活MNase,將DNA片段釋放到上清液中。CUT&RUN片段用蛋白酶K處理1小時,然后分離DNA進行測序。
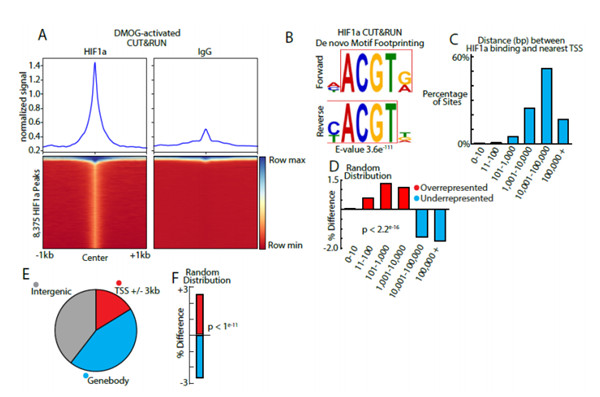
在HIF1α激活后,CUT&RUN在原代晶狀體細胞中鑒定了8000多種HIF1α-DNA特異性復合物。他們能夠使用ATAC-seq和RNA-seq驗證并完成結(jié)合位點的映射,這表明這些復合物中約有1200個緊密聚集在染色質(zhì)可及區(qū)域。進一步的分析揭示了526個基因的激活或抑制,其中116個基因在轉(zhuǎn)錄起始位點10kB內(nèi)顯示HIF1α結(jié)合位點。
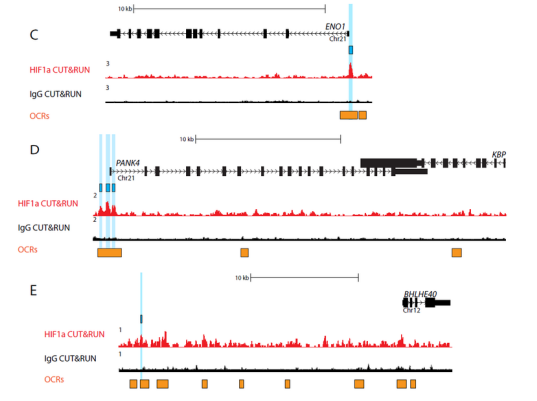
該實驗中收集的數(shù)據(jù)有助于建立眼晶狀體中HIF1αDNA復合物的第一個功能圖,同時也強調(diào)了健康晶狀體發(fā)育對HIF1α的需求。最終,CUT&RUN技術(shù)的這種成功應用,有助于接下來的大量研究,重點是了解某些蛋白質(zhì)可能對基因表達的作用。
產(chǎn)品推薦
艾美捷科技作為表觀遺傳領域?qū)I(yè)的解決方案供應商,為您推薦EpiGentek品牌的EpiNext EpiNext CUT&RUN快速套件,貨號P-2028,該試劑盒以優(yōu)惠價格從低輸入提供無超聲破碎,以可靠地識別真正的目標蛋白質(zhì)富集區(qū)域并實現(xiàn)高分辨率定位。可滿足您快速富集蛋白質(zhì)結(jié)合的DNA并繪制全基因組蛋白質(zhì)/DNA相互作用的圖譜的需求。
從哺乳動物細胞或分離的細胞核/染色質(zhì)開始進行成功的CUT RUN所需的一整套優(yōu)化試劑。該試劑盒被設計成快速富集具有來自低輸入細胞/染色質(zhì)的蛋白質(zhì)(組蛋白或轉(zhuǎn)錄因子)的特定DNA復合物,并通過下一代測序使用Illumina平臺或其他方法如qPCR鑒定或繪制體內(nèi)蛋白質(zhì)-DNA相互作用。創(chuàng)新的工作原理、優(yōu)化的方案和試劑盒的組件允許捕獲靶向蛋白質(zhì)/DNA復合物與最小化的非特異性背景水平。
| 貨號 | 名稱 | 廠家 | 時長 |
| P-2028 | EpiNext CUT&RUN快速套件 EpiNext CUT&RUN Fast Kit | Epigentek | <3小時 |
結(jié)果展示
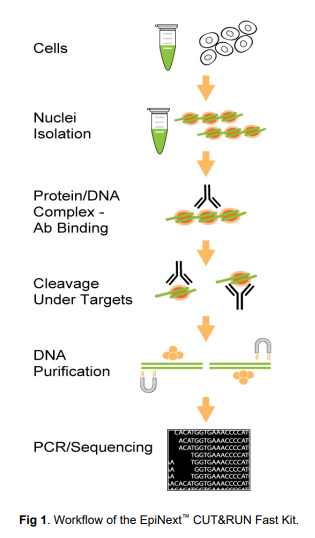
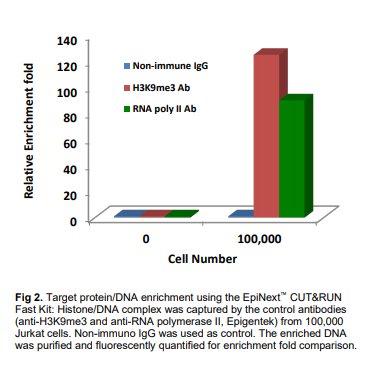
EpiNext CUT&RUN快速套件優(yōu)勢:
1、高富集:使用獨特的核酸切割酶混合物,其具有低序列偏好,以同時片段化染色質(zhì)并切割/去除靶蛋白/DNA復合物兩端的任何DNA序列,而不影響靶蛋白占據(jù)的DNA。富集的DNA 20 bp可被高效、快速地回收。因此,靶蛋白富集區(qū)域可以可靠地獲得和在高分辨率作圖中鑒定。
2、低輸入材料:穩(wěn)健的無超聲破碎、未結(jié)合的DNA切割和免疫捕獲都在相同的單管中進行處理,具有珠上連接。該方法使用細胞和組織兩者,并且允許靶蛋白的最大降解保護,且樣品損失最小。因此,輸入細胞量可以少至500個細胞,或者染色質(zhì)量可以低至0.1 ?g。
3、最小背景:原位切割靶蛋白質(zhì)/DNA復合物的兩(2)末端中未結(jié)合的DNA序列使得免疫捕獲背景最小化,從而允許具有1000萬個讀段的測序數(shù)據(jù)分析<。
4、快速、簡化的程序:從細胞到文庫DNA的過程少于3小時。
5、非常方便:該套件包含切割運行每個步驟所需的所有組件&,從而使EpiNext?切割&運行快速套件最方便,結(jié)果可靠且一致。

微信掃碼在線客服