TECHNICAL COLUMN
學(xué)習(xí)資源當(dāng)前位置:首頁(yè) > 學(xué)習(xí)資源
在當(dāng)前生物技術(shù)領(lǐng)域中,CRISPR-Cas9技術(shù)已經(jīng)成為基因編輯的重要工具。本文旨在提供一份詳細(xì)的CRISPR-Cas9實(shí)驗(yàn)教程,從gRNA設(shè)計(jì)到單克隆挑選的全過(guò)程指導(dǎo)。通過(guò)本文,您將了解到如何設(shè)計(jì)高效的gRNA序列,掌握CRISPR-Cas9系統(tǒng)的原理與操作步驟,并學(xué)會(huì)如何進(jìn)行單克隆篩選,確保實(shí)驗(yàn)結(jié)果的準(zhǔn)確性和可靠性。無(wú)論您是初學(xué)者還是有一定經(jīng)驗(yàn)的研究人員,本文都將為您提供全面的指導(dǎo),幫助您成功應(yīng)用CRISPR-Cas9技術(shù)進(jìn)行基因編輯研究。
基本原理
CRISPR-Cas9是一種細(xì)菌天然免疫系統(tǒng),用于針對(duì)外源DNA進(jìn)行有針對(duì)性的降解。它的工作機(jī)制是通過(guò)CRISPR RNA (crRNA) 和轉(zhuǎn)錄激活crRNA (trans-activating crRNA,tracrRNA) 之間的互補(bǔ)配對(duì)形成復(fù)合物,能夠特異性識(shí)別基因組中與其互補(bǔ)的序列。這種復(fù)合物可以引導(dǎo)Cas9內(nèi)切酶切割目標(biāo)DNA片段,導(dǎo)致DNA雙鏈斷裂的形成。這一過(guò)程實(shí)現(xiàn)了對(duì)目標(biāo)基因組的精確編輯和修飾。如下圖所示:
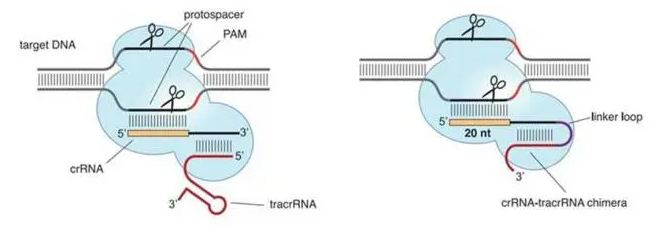
通過(guò)基因工程手段對(duì)crRNA和tracrRNA進(jìn)行改造,將其連接在一起得到sgRNA (single guide RNA)。通過(guò)將表達(dá)sgRNA的原件與表達(dá)Cas9的原件相連接,得到可以同時(shí)表達(dá)兩者的質(zhì)粒,將其轉(zhuǎn)染細(xì)胞,便能夠?qū)δ康幕蜻M(jìn)行基因操作,在PAM (5’-NGG) 上游 ~3bp進(jìn)行切割,如下圖所示:
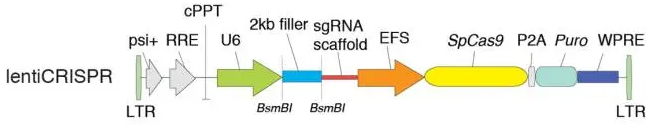
因此本實(shí)驗(yàn)的關(guān)鍵步驟是設(shè)計(jì)一對(duì)20bp(不包括NGG在內(nèi)的)完全互補(bǔ)的oligo插入到如上圖所示的filler。另U6啟動(dòng)子需要5’端的G起始轉(zhuǎn)錄,因此若設(shè)計(jì)的oligo第一個(gè)堿基非G,需額外增加一個(gè)G。
詳細(xì)操作流程
1. 設(shè)計(jì)sgRNA
確定靶基因的序列后,可通過(guò)在線網(wǎng)站設(shè)計(jì)(http://tools.genome-engineering.org ),或根據(jù)靶基因的CDS序列自行設(shè)計(jì),最方便的是在human KO Library sgRNA里選擇。無(wú)論選擇哪種方式,都建議進(jìn)行一下blast。
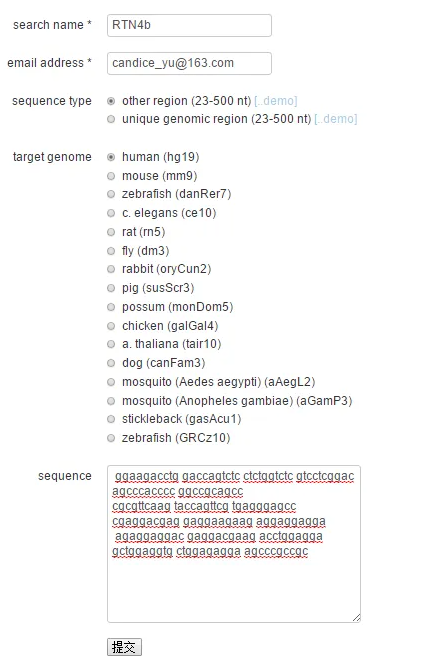
附上在線設(shè)計(jì)網(wǎng)頁(yè)截圖。輸入基因的name,填寫email address,設(shè)計(jì)結(jié)果稍后會(huì)發(fā)送到此郵箱,選擇序列的類型以及物種。如sequence type選擇unique region,一次只能輸入23~500bp的基因片段,最好一次只輸入一個(gè)外顯子,避免guide序列跨越內(nèi)含子,都選擇鍵入后點(diǎn)擊提交,關(guān)注郵箱或者在線等。
分析中,顯示你所鍵入的基因序列里有36對(duì)可選的guide序列。
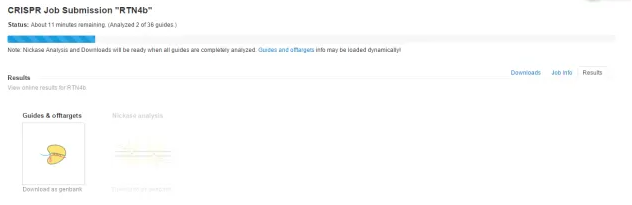
分析結(jié)束,點(diǎn)擊Download as genbank查看結(jié)果,此時(shí)也會(huì)收到郵件。
選擇分?jǐn)?shù)較高的Guide序列,以Guide#1序列為例,2條單鏈oligo的序列如下:oligo1:5’- caccGCGTTCAAGTACCAGTTCGTG -3’; oligo2:5’- aaacCACGAACTGGTACTTGAACGc。標(biāo)粗部分與經(jīng)BsmBI酶切后的載體互補(bǔ)配對(duì)。BsmBI又名BbsI。

※oligoDNA序列的第一個(gè)堿基必須是G,如選取的Guide序列的第一個(gè)堿基不是G,需自行添加一個(gè)額外的G。

2. Oligo退火形成duplex

PCR儀 95℃ 5 min,緩慢降溫至室溫1h,1:200稀釋duplex。
3. 質(zhì)粒酶切

4. 膠回收
大片段約11kb 回收;小片段約2kb為切下來(lái)的filler,不要。
5. 連接

室溫連接4-6 h。
6. 轉(zhuǎn)化(Amp+),挑克隆,搖菌,抽提質(zhì)粒,測(cè)序!
7. 轉(zhuǎn)染
24孔板,細(xì)胞不要過(guò)滿,同實(shí)驗(yàn)室日常轉(zhuǎn)染操作,可選擇性設(shè)置三個(gè)平行。同時(shí)轉(zhuǎn)染空載作為陰性對(duì)照。每孔500 ng。
8. puromycin篩選
轉(zhuǎn)染穩(wěn)定48-72h后加puromycin進(jìn)行篩選,1~3?g/mL,直至不再有細(xì)胞數(shù)量穩(wěn)定,不再有細(xì)胞因不耐藥死去。
9. 單細(xì)胞分離
由于篇幅原因,有限稀釋法具體細(xì)節(jié)會(huì)在后面的文章單獨(dú)講解,請(qǐng)關(guān)注科研小助手后續(xù)文章。100個(gè)細(xì)胞鋪在一個(gè)大盤或96孔板中。剩余的細(xì)胞凍存。
10. 獲得單克隆細(xì)胞株
當(dāng)肉眼可見(jiàn)類似于菌落的細(xì)胞團(tuán)時(shí),將其從大盤或96孔板消化下來(lái)轉(zhuǎn)移至12或24孔板中繼續(xù)擴(kuò)大培養(yǎng)。注意不要污染到其它細(xì)胞團(tuán),不要選取過(guò)密的細(xì)胞團(tuán)。
11. 擴(kuò)大培養(yǎng),提取細(xì)胞全基因組DNA和細(xì)胞總蛋白
12. 測(cè)序
Guide序列上游100bp左右和下游200bp左右為上下游設(shè)計(jì)一對(duì)引物,以全基因組為模板,以上述引物進(jìn)行PCR。PCR產(chǎn)物送測(cè)序,或?qū)a(chǎn)物用T7E1進(jìn)行酶切消化檢測(cè)突變。
13. Western
與陰性對(duì)照相比,靶基因應(yīng)完全敲除

微信掃碼在線客服